
전장유전체 정밀분석으로,
암의 전체 모습을 명확히 밝힙니다
CancerVision은 tumor–normal paired samples 기반의 전장유전체 암 프로파일링 검사입니다. 99%의 민감도와 복합 변이의 정확한 탐지 및 정밀한 시그니처 분석을 단 한 번의 검사로 제공합니다.
전장유전체의
포괄적 분석 범위
coding,non-coding 영역 전반에서
40× Tumor, 20× germline sequencing을 통해 CNV, SV 복합 구조 변이 등 모든 변이 유형을 정확히 탐지합니다.
타깃 영역의
심층 분석 강화
600개 이상의 임상 관련 유전자에 대해
500× 커버리지로 깊이 있게 분석하여,
WGS의 폭넓은 범위와 패널의 정확성을
모두 갖춘 정밀 진단을 제공합니다.
임상적으로
검증된 성능
CAP/CLIA 인증 검사로 SNV 99%,
Indel 98% 이상의 민감도와
양성예측도를 확보했으며,
결과는 2주 이내에 제공합니다
복잡한 변이의
정밀 탐지
CNV, SV, non-coding 영역까지 포괄하는
정밀 분석
유전체 전반의 변이 양상
모든 종양 유형에서
TMB, MSI, HRD 분석
맞춤형 전장유전체 분석
요청 시 ecDNA, 종양 배수성, 전이성 유전요소 등의 맞춤 분석 제공
CAP/CLIA 인증 검사
2주 이내 결과 제공
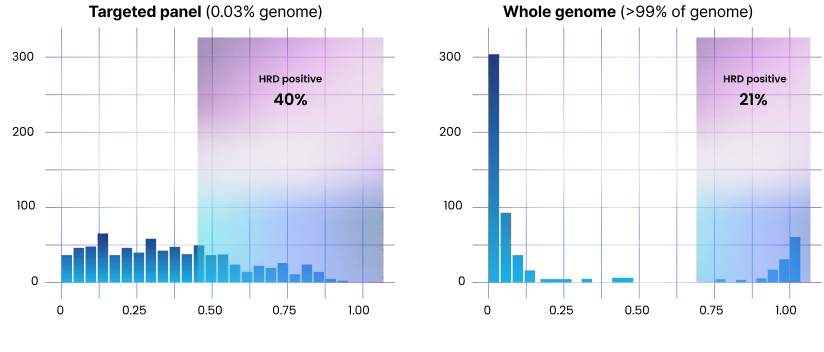
CancerVision과 타깃 패널 기반 HRD 점수 비교
1 Ju, Y. S et al, (2024). Whole-Genome analyses of 1,364 breast cancers with clinical records. Research Square(Preprint). https://doi.org/10.21203/rs.3.rs-5094752/v1
보다 정확한 전장유전체 기반
바이오 마커 1,364건의 유방암
HRD 사례
CancerVision은 전장유전체 기반 분석으로 HRD 양성과 음성을 더욱 명확히 구분합니다. HRD를 포함한 유전체 전반의 마커 분석이 기본으로 제공됩니다.
CancerVision과 함께 더 빠르고, 정밀한 연구를 실현하세요.
For cancer researchers
Complete genimic Profiling
Identify information that may be potentially missed by WES/TPS
Genome-wide analysis for instability markers
Get a comprehensive view of genomic instability markers with an all-inclusive whole-genome snapshot for accurate detection of TMB, MSI and HRD status
Tumor-specific alterations vs. inherited sequences
Distinguish between tumor-specific vs. inherited genetic alterations across diverse populations germline
Custom analysis for whole-genome biomarkers
Bioinformatics support for whole genome based biomarkers – whole genome doubling, ecDNA, tumor ploidy, MATH score, and more.
For biopharma
Novel biomarker discovery
Leverage whole genome data to uncover previously invisible biomarkers, including genome-wide mutational signatures and non-coding alterations
Novel patient subgroups
Identify responder and non-responder populations for targeted therapies using whole genome insights, enabling more precise patient stratification and higher trial success rates
Accelerated clinical trial enrollment
Rapidly identify and enroll patients for clinical trials by capturing mutations of interest across SNVs, indels, CNVs, SVs, and non-coding regions—speeding up trial timelines
Future-proofed trials
Access comprehensive whole genome data, ensuring readiness for post-phase II/III analyses without the need for additional samples or sequencing
분석 가능 검체 및 요구사항
| Somatic specimen | Volume | Shipping condition |
|---|---|---|
| FFPE tissue | ≥10 from curls or slides in 5 micron thickness, with an H&E stained slide for reference | Ambient |
| Fresh frozen | 25mg of cryopreserved tissue | Frozen or dry ice |
| Germline specimen | Volume | Shipping condition |
|---|---|---|
| Whole blood | 1 Streck or EDTA tube – minimum of 2mL | Ambient or with cold packs |
| gDNA | ≥100ng – minimum concentration of 2ng/uL | Ambient or frozen |
| Saliva | 1 tube in collection device | Ambient |
| Buccal swab | 1 swab in fixative solution | Ambient |